MTD 243-670 Bedienungsanleitung Seite 46
- Seite / 101
- Inhaltsverzeichnis
- LESEZEICHEN
Bewertet. / 5. Basierend auf Kundenbewertungen


5 Ergebnisse
40
Signal, wodurch eine Wechselwirkung der Sonde mit der Vektorsequenz
auszuschließen war.
Sonde I
1
bp
2000 bp
Eco RV
Eco RV
Eco RV
1200 bp
sdmA
2000
1200
1031
3000
1500
A B
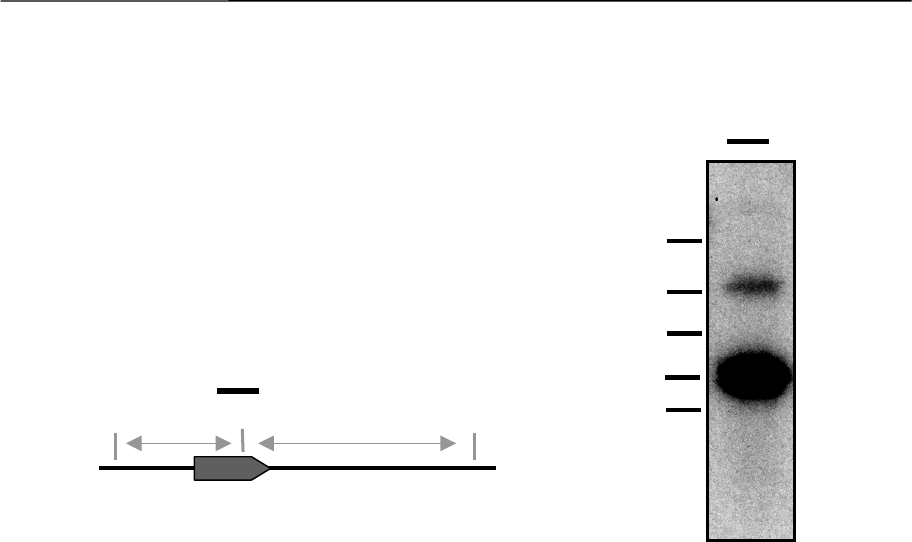
Abb. 6: Southern-Blot-Analyse des Gens sdmA
A: Schematische Darstellung der Schnittstellen von Eco RV in der chromosomalen DNA von M. voltae
aus dem Bereich um das Gen sdmA.
B: 5 µg chromosomale DNA von M. voltae wurden mit Eco RV behandelt und in einer Southern-Blot-
Analyse untersucht. Für die Hybridisierung wurde die Sonde I verwendet. Die Bindestelle der Sonde
ist in der schematischen Darstellung angedeutet. bp: Längenstandard in Basenpaaren.
5.3 Im 3´-Bereich des Gens sdmA liegen die offenen Leseraster
sdmB und sdmC
An den aus den verschiedenen Screeningverfahren erhaltenen Klone wurde die
Sequenz des 5´- und 3´-Bereichs des Gens sdmA mit den Standard-
Sequenzierprimern M13fw und M13rv teilweise ermittelt. Die Bindestellen dieser
Oligonukleotide findet man in den gängigen Vektoren und sie ermöglichen die
Sequenzierung eines eingefügten Fragments, wenn es von diesen Stellen flankiert
ist. Bei sehr großen Inserts ist die Sequenzierung allein mit den Standardprimern
nicht mehr möglich. Die Sequenz von sdmA und des umgebenden Bereichs, die
durch M13fw und M13rv nicht ermittelt werden konnte, wurde mit den Primern
ird800corri25, ird800P2walker5B, corrimet16RV und corrimet16FW bestimmt. Dabei
- auf Selenmangel 1
- Inhaltsverzeichnis 4
- TÄMME V1 UND V1 6
- 1 Abkürzungsverzeichnis 7
- 2 Zusammenfassung 9
- 3 Einleitung 11
- 4 Material und Methoden 22
- 4.5 Oligonukleotide 23
- 4 Material und Methoden 24
- 4.6 Phagenbank 25
- 4.7 Plasmide 25
- 5807 bp 28
- 4.9.11 Primer Extension 33
- 4.9.12 RT-PCR 34
- 4.9.18 Southern-Blot-Analyse 36
- 4.9.21 Northern-Blot-Analyse 38
- 5 Ergebnisse 42
- Gens sdmA 53
- RTmetIIfw 70
- RTmetIIB 70
- RTmetIIr 70
- RTpac RTmetIrvB 70
- 6 Diskussion 71
- 7 Literaturverzeichnis 84
- Lebenslauf : 100
 (144 Seiten)
(144 Seiten) (56 Seiten)
(56 Seiten)







Kommentare zu diesen Handbüchern